
【編集部注】著者のMahni GhorashiはClear Labsの共同創業者である。彼はそこで戦略、マーケティングおよび事業開発を含む商業活動を統括している。共著者のGaurav GargはWing Venture Capitalの創業パートナーである。
私たちは、全ゲノムシーケンシング(WGS)の歴史の、新たな段階に入った。トロント大学の研究者たちが、年に1万人分の全ゲノム配列を決定する大規模なプロジェクトを立ち上げたことを考えて欲しい。最初の1人分のゲノムの配列を解析するのに13年の年月と30億ドルのコストがかかったことを考えると、これは本当に驚くべきことだ。2012年の段階ですら、わずかに69人分の全ゲノム配列が決定されていただけなのだ。
最初にWGSが患者の治療の際の参考として用いられた2010年から、私たちはWGSを医療のパーソナライズのために利用してきた。
今では私たちの公的および私的レファレンスデータベースが成長し、より多くのゲノムデータにアクセスできるようになったことで、WGSの潜在能力を最大限に発揮するための機械学習の利用が始まろうとしている。機械学習能力と利用可能な処理能力の増加は、遺伝子研究だけでなく、多くの産業にまたがるゲノム学の幅広い応用を促進している。私たちは今まさに、農業と食品の安全性のような他の産業分野で、次世代シーケンシング(NGS)のような最先端WGS技術が始まっているのを目撃している。
特に機械学習のような技術的治療法と組み合わせるに当たり、応用科学としてのWGSの重要性をより深く理解し、今後数年間にWGSが様々な産業をいかに迅速に変えていくかをよりよく理解するために、基本的なシーケンシングと分析技術がどのように発展して来たかを理解しておくことは役に立つだろう。
WGSの簡単な歴史
WGSとヒトDNAの研究を関連付けることが普通になっているが、もちろんWGSは、あらゆる生物の完全なDNA配列を明らかにするために利用できる実験室プロセスだ。実際その全ゲノム配列が決定された最初の生物はヒトの気道に生息するインフルエンザ菌(Haemophilus influenzae)であった(なおインフルエンザ菌はその名前に関わらずインフルエンザの真の原因ではない)。 このブレークスルーは1995年に達成された。キイロショウジョウバエ(Drosophila melanogaster)のゲノム配列が研究者たちの手で解析されたのは、丸5年後の2000年のことだ。
ヒトゲノム計画プロジェクトがヒトゲノムの全配列を発表したのは、3年後の2003年だった。科学の歴史の中で、他の最も重要なブレークスルーたちと比べても引けをとらないこの重大な成果には、およそ30億ドルの費用と13年の超人的労力が必要とされた。
2005年に次世代シーケンシング(NGS)が導入されるまで、WGSの商業化には多くの疑問が残されていた。NGSとは、従来のサンガーシーケンシング技術の大部分を置き換える、様々なシーケンシング技術を総称する用語である。
WGSが示す可能性は、人間の健康の未来に大きな影響を与える。
Illumina、Roche、Life Technologiesなど多くの企業で開発されたこれらの技術は、DNAとRNAのシーケンシングの時間とコストを大幅に削減し、ゲノム学と分子生物学の研究と応用に革命をもたらした。この1年ほどの動きを見ると、私たちは間もなく1人の人間の全ゲノムを1000ドルで解析することができそうだ。実際Veritas Geneticsが、1000ドル以下で人間のゲノムの配列を決定し、解析し、解釈できた初の企業として賞賛されている。
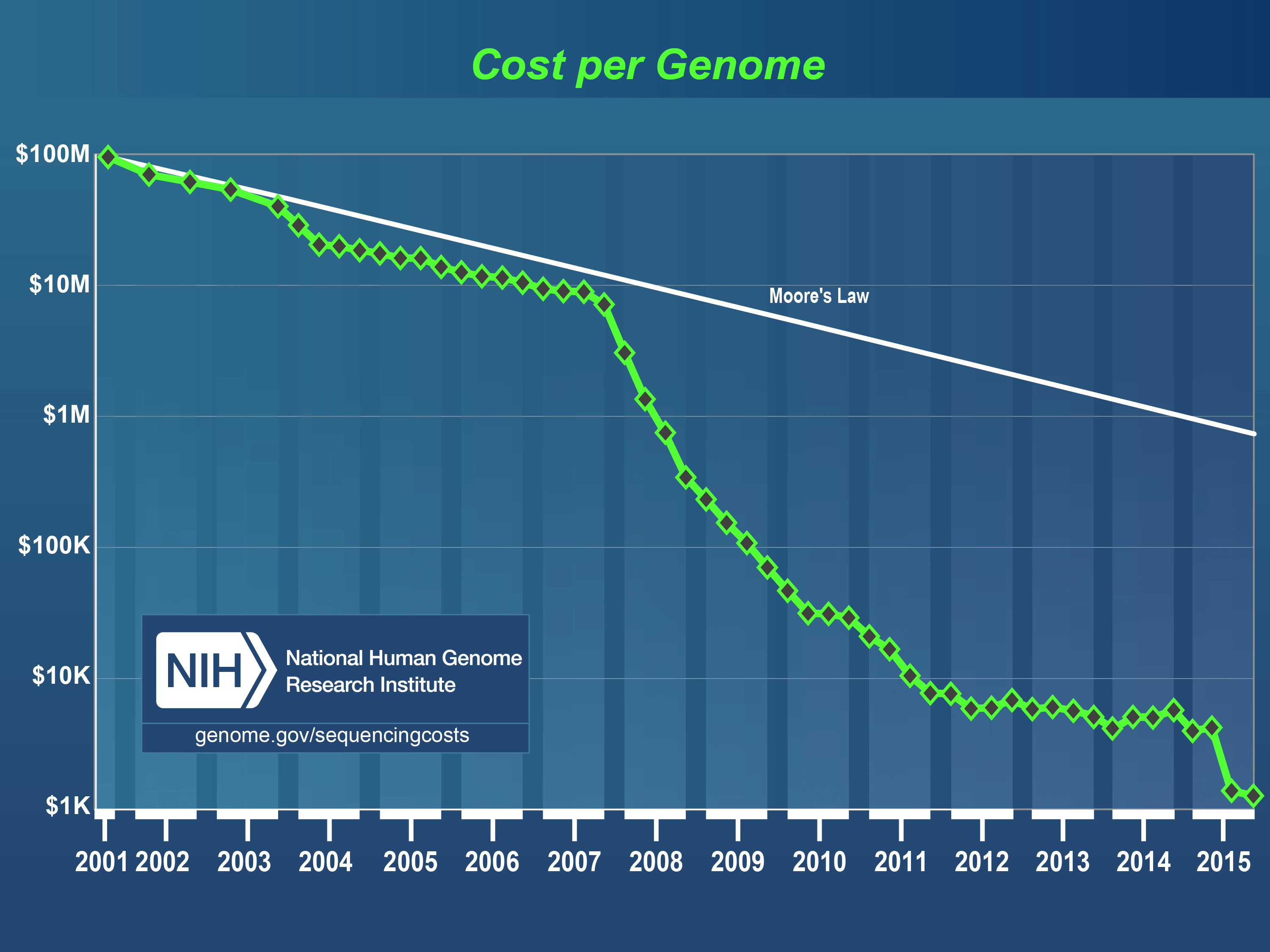
出典:米国立ヒトゲノム研究所(National Human Genome Research Institute)
1000ドルという数字自体には大きな意味はない。本当に重要なことは、私たちは今や、例えばトロント大学で構築されているデータベースのような、研究者が必要とする大規模なデータベースを構築するために、人間のゲノムの配列を素早く安価に決定することができるということだ。こうしたデータベースを用いることによって、複雑な疾病をより良く理解することができ、遺伝子がお互いにどのように関係しているのか、遺伝子が環境の変化にどのように反応しているのかを知ることができる。
配列決定は、最初の一歩にすぎない:現代のゲノム学におけるデータ科学の役割
NGSの導入以来、WGSの時間とコストの削減は、主にコンピュータエンジニアリングの問題となっている。ヒトゲノムの生データを医学的に有用かつ理解可能な情報に変換することは、歴史的に見て大きな技術的ボトルネックだったが、過去10年にわたって、実験室の技術ではなく計算の進歩が、WGSに関わる時間とコストを最大に削減してきた。ムーアの法則は死んだかも知れないが、光学コンピューティングがゲノム処理を改善し続けている。
例えば、カンザスシティのChildren’s Mercy病院は、2015年に行われた遺伝子疾患の緊急管理に関する研究の中で、完全な解析を含む完全ゲノム配列を使用したことを詳細に報告している。LlluminaのHiSeqマシン、そしてEdico GenomeのDRAGENプロセッサとカスタマイズされたソフトウェアを用いて、病院のチームはわずか26時間で配列を決定し解析したのだ。DRAGENプロセッサだけでも、解析時間は15時間から40分に短縮された。
さてここで言う解析とは何だろう。まず初めに、第1、第2および第3の解析が区別される。今日の近代的なシーケンサーは、生の化学的および物理的サンプルを、最初の生の配列データへと変換する。この最初の変換プロセスを、私たちは1次解析と呼ぶ。
私たちはデータを取り込むが、そのままでは分かりにくい。
2次解析は、ゲノムを組み立てるプロセスだ。10億ピースのジグソーパズルを解こうとしていると想像して欲しい。シーケンサーは全ての塩基対を示すが、それらは正しい順序では並んでいない。想像できるように、これは計算集約型のプロセスだ。2次解析の最終結果は、全ゲノムに相関したデータとなる。
例えばある疾病に対する突然変異を特定するといった、遺伝子データから意味を抽出するためには、3次解析が必要となる。ゲノム学の応用が始まるのはここからだ。これは無数のソフトウェア・ソリューションが考えられるビッグデータ問題でもある。
将来の技術革新のための最も肥沃な土地は、全ゲノムから意味を抽出するための新しい方法とワークフローを工夫する場所に広がっている。私たちはデータを取り込むが、そのままでは分かりにくい。
健康に対するWGSの未来
WGSは、ヘルスケアシステムの運営方法、そして消費者が自身の健康を管理する方法の両面で、人間の健康の未来に大きな影響を与える。
制度のレベルで考えた場合、ゲノム学の力は納税者たちや為政者に、人びとの健康を増進する上で興味深い役割を果たす。ほとんどのヘルスケア提供者は依然として、愁訴データおよび電子カルテにある治療履歴情報にほぼ依存している。こうした履歴情報は、本来予防可能な慢性疾患を既に発症している人びとの10から15%を教えてくれるものの、残りの人びとの中で、発症の条件が高まっているリスクに瀕している人に関しては、何も教えてくれない。ゲノム学は、特定の疾患を発症するリスクが高い人の特定を助け、早期に介入できるようにする。
消費者レベルでは、パーソナライズ医療が引き続きWGSの主要な焦点になる。特に、人間の遺伝的変異の大部分が未だ解釈されていないことを思えば、やるべきことはまだまだ沢山ある。私たちは、他の参照ゲノムと比較することで、個人の遺伝子データから意味を抽出することができる。そしてより多くの参照ゲノムを扱えば扱うほど、私たちのソフトウェアとプロセスも改善されて行く。遺伝子データの巨大なデータベースを構築するための計画が、この仕事の将来にとっての基礎なのだ。
この研究が切り拓く、他のヘルスケア上の応用も考えられる。最も興味深いものの一つは、個々人の微生物叢構成の理解に基づく高精度の栄養管理だ。いわゆる善玉菌(さらには善玉菌によい食物)は、固有の微生物叢に基づく大きな影響を個人に及ぼすことができる。パーソナライズ医療が既存のNGS手法から現れたように、個人向けの最適化された栄養管理を行うための、人間の微生物叢を分析する新しい実験的NGS手法の出現が期待できる。
WGSによる可能性のスペクトルは、医師のオフィスから在宅ケアをカバーする幅広い医療に影響を持っている。
健康を超えて
NGSと高性能コンピューティングの革新がゲノムシーケンシング全体のコストを引き下げ続けているため、ゲノムのデータと洞察は、医療や医薬品以外の産業にも変革をもたらす。
農業ゲノム学は、シーケンシングと解析の革新によって拓かれつつある新興市場の1つだ。例えばDe novoシーケンシング法は、位置合わせのために利用可能な参照シーケンスがない場合でも、新たなゲノムを配列決定することができる革新的なNGS技術だ。農業ゲノム学研究者はすでに、植物または動物の遺伝的変異を発見し、機能と環境との相互作用の遺伝的基盤を明らかにするために、De novoシーケンシング法を用いて、ゲノムの組み立てを行っている。
DNAを用いてデータを保存する実験を始めている研究者たちもいる。昨年の初め、Microsoftとワシントン大学の研究者らは、200MBのデータを合成DNA上へエンコードし、それを再び読み出してみせた。実はDNAは、究極の記憶媒体だ。耐久性が高くコンパクトだというのがその理由だ。全世界のデータを1キロのDNAでエンコードできると考える専門家もいる。
遺伝子情報革命
ゲノム学が約束する未来は、まだ現れ始めたばかりだ。私たちはシーケンシングと解析技術がもたらす、遺伝子情報革命の最先端にいる。
WGSは、私達の世界全体を、分子レベルで理解するための扉を開いた。こうした情報に恵まれた私たちは、私たち自身並びに自然界との対話方法を、単に理解するだけではなく、影響を与え最適化するようになるだろう。
[ 原文へ ]
(翻訳:Sako)